Attention: World-2DPAGE is no longer maintained.
[Click to access protein entry]
Spot: 2D-001HI9 (ecoli4-5)
pI: 4.63 Mw: 45613
%vol: 0.356594 %od: 0.6142
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 931.451 (0), 1003.472 (0), 1036.541 (0), 1101.499 (0),
1191.564 (0), 1420.717 (0), 1440.777 (0), 1561.762 (0), 1614.789 (0),
1617.771 (0), 1671.746 (0), 1687.696 (0), 1742.88 (0), 1756.807 (0),
2085.061 (0), 2249.052 (0), 2338.074 (0), 2566.175 (0), 2629.214 (0)
}
Spot: 2D-001HI9 (ecoli4-5)
pI: 4.63 Mw: 45613
%vol: 0.356594 %od: 0.6142
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 931.451 (0), 1003.472 (0), 1036.541 (0), 1101.499 (0),
1191.564 (0), 1420.717 (0), 1440.777 (0), 1561.762 (0), 1614.789 (0),
1617.771 (0), 1671.746 (0), 1687.696 (0), 1742.88 (0), 1756.807 (0),
2085.061 (0), 2249.052 (0), 2338.074 (0), 2566.175 (0), 2629.214 (0)
}
[Click to access protein entry]
Spot: 2D-001HJP (ecoli4-5)
pI: 4.97 Mw: 39311
%vol: 0.213753 %od: 0.317423
================
*GALM_ECOLI*
accession n°: P0A9C3
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1086.468 (0), 1492.73 (0), 2347.178 (0), 2684.299 (0),
2755.335 (0) }
Spot: 2D-001HJP (ecoli4-5)
pI: 4.97 Mw: 39311
%vol: 0.213753 %od: 0.317423
================
*GALM_ECOLI*
accession n°: P0A9C3
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1086.468 (0), 1492.73 (0), 2347.178 (0), 2684.299 (0),
2755.335 (0) }
[Click to access protein entry]
Spot: 2D-001HQU (ecoli4-5)
pI: 4.80 Mw: 9699
%vol: 0.219364 %od: 0.0758436
================
*THIO_ECOLI*
accession n°: P0AA25
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1001.692 (0), 1267.702 (0), 1731.905 (0), 1805.908 (0),
1821.916 (0) }
Spot: 2D-001HQU (ecoli4-5)
pI: 4.80 Mw: 9699
%vol: 0.219364 %od: 0.0758436
================
*THIO_ECOLI*
accession n°: P0AA25
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1001.692 (0), 1267.702 (0), 1731.905 (0), 1805.908 (0),
1821.916 (0) }
[Click to access protein entry]
Spot: 2D-001HFW (ecoli4-5)
pI: 4.95 Mw: 60559
%vol: 1.12029 %od: 1.98491
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {Gm} {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 944.482 (0), 952.459 (0), 960.461 (0), 1021.532 (0),
1050.497 (0), 1149.62 (0), 1179.593 (0), 1206.57 (0), 1267.695 (0),
1277.64 (0), 1286.676 (0), 1299.647 (0), 1395.759 (0), 1427.797 (0),
1485.804 (0), 1500.79 (0), 1598.804 (0), 1659.865 (0), 1815.939 (0),
1960.963 (0), 2280.975 (0), 2372.132 (0), 2423.22 (0), 2441.23 (0),
2532.193 (0), 2640.16 (0), 2653.203 (0) }
Spot: 2D-001HFW (ecoli4-5)
pI: 4.95 Mw: 60559
%vol: 1.12029 %od: 1.98491
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {Gm} {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 944.482 (0), 952.459 (0), 960.461 (0), 1021.532 (0),
1050.497 (0), 1149.62 (0), 1179.593 (0), 1206.57 (0), 1267.695 (0),
1277.64 (0), 1286.676 (0), 1299.647 (0), 1395.759 (0), 1427.797 (0),
1485.804 (0), 1500.79 (0), 1598.804 (0), 1659.865 (0), 1815.939 (0),
1960.963 (0), 2280.975 (0), 2372.132 (0), 2423.22 (0), 2441.23 (0),
2532.193 (0), 2640.16 (0), 2653.203 (0) }
[Click to access protein entry]
Spot: 2D-001HFY (ecoli4-5)
pI: 4.95 Mw: 60700
%vol: 0.210692 %od: 0.100779
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 875.371 (0), 1050.479 (0), 1149.603 (0), 1179.61 (0),
1201.642 (0), 1206.584 (0), 1277.66 (0), 1485.821 (0), 1598.836 (0),
2281.105 (0), 2441.288 (0), 2653.333 (0) }
Spot: 2D-001HFY (ecoli4-5)
pI: 4.95 Mw: 60700
%vol: 0.210692 %od: 0.100779
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 875.371 (0), 1050.479 (0), 1149.603 (0), 1179.61 (0),
1201.642 (0), 1206.584 (0), 1277.66 (0), 1485.821 (0), 1598.836 (0),
2281.105 (0), 2441.288 (0), 2653.333 (0) }
[Click to access protein entry]
Spot: 2D-001HFZ (ecoli4-5)
pI: 4.48 Mw: 59582
%vol: 0.143352 %od: 0.114465
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 960.401 (0), 1149.611 (0), 1179.596 (0), 1206.551 (0),
1395.789 (0), 1485.793 (0), 1598.835 (0), 2532.328 (0), 2653.348 (0)
}
Spot: 2D-001HFZ (ecoli4-5)
pI: 4.48 Mw: 59582
%vol: 0.143352 %od: 0.114465
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 960.401 (0), 1149.611 (0), 1179.596 (0), 1206.551 (0),
1395.789 (0), 1485.793 (0), 1598.835 (0), 2532.328 (0), 2653.348 (0)
}
[Click to access protein entry]
Spot: 2D-001HH2 (ecoli4-5)
pI: 4.84 Mw: 52802
%vol: 0.129068 %od: 0.0925646
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1045.564 (0), 1454.728 (0), 1567.962 (0), 1711.934 (0),
1761.053 (0), 1846.106 (0) }
Spot: 2D-001HH2 (ecoli4-5)
pI: 4.84 Mw: 52802
%vol: 0.129068 %od: 0.0925646
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1045.564 (0), 1454.728 (0), 1567.962 (0), 1711.934 (0),
1761.053 (0), 1846.106 (0) }
[Click to access protein entry]
Spot: 2D-001HQJ (ecoli4-5)
pI: 4.87 Mw: 9851
%vol: 0.187225 %od: 0.186837
================
*RL7_ECOLI*
accession n°: P0A7K2
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 964.529 (0), 1113.594 (0), 1244.623 (0), 1261.591 (0),
2015.009 (0) }
Spot: 2D-001HQJ (ecoli4-5)
pI: 4.87 Mw: 9851
%vol: 0.187225 %od: 0.186837
================
*RL7_ECOLI*
accession n°: P0A7K2
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 964.529 (0), 1113.594 (0), 1244.623 (0), 1261.591 (0),
2015.009 (0) }
[Click to access protein entry]
Spot: 2D-001HLA (ecoli4-5)
pI: 5.00 Mw: 26823
%vol: 0.176512 %od: 0.0487812
================
*GLNA_ECOLI*
accession n°: P0A9C5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 922.452 (0), 1107.568 (0), 1184.524 (0), 1200.499 (0),
1579.716 (0), 1636.754 (0), 1717.847 (0), 2004.902 (0), 2310.093 (0),
2495.221 (0), 2586.265 (0), 3113.389 (0) }
Spot: 2D-001HLA (ecoli4-5)
pI: 5.00 Mw: 26823
%vol: 0.176512 %od: 0.0487812
================
*GLNA_ECOLI*
accession n°: P0A9C5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 922.452 (0), 1107.568 (0), 1184.524 (0), 1200.499 (0),
1579.716 (0), 1636.754 (0), 1717.847 (0), 2004.902 (0), 2310.093 (0),
2495.221 (0), 2586.265 (0), 3113.389 (0) }
[Click to access protein entry]
Spot: 2D-001HIA (ecoli4-5)
pI: 4.98 Mw: 45932
%vol: 0.154065 %od: 0.0432561
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 876.417 (0), 931.528 (0), 1003.547 (0), 1036.539 (0),
1101.547 (0), 1191.628 (0), 1234.704 (0), 1420.746 (0), 1561.816 (0),
2249.1 (0), 2338.112 (0), 2566.267 (0) }
Spot: 2D-001HIA (ecoli4-5)
pI: 4.98 Mw: 45932
%vol: 0.154065 %od: 0.0432561
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 876.417 (0), 931.528 (0), 1003.547 (0), 1036.539 (0),
1101.547 (0), 1191.628 (0), 1234.704 (0), 1420.746 (0), 1561.816 (0),
2249.1 (0), 2338.112 (0), 2566.267 (0) }
[Click to access protein entry]
Spot: 2D-001HMA (ecoli4-5)
pI: 5.00 Mw: 20965
%vol: 0.214263 %od: 0.169117
================
*YJDC_ECOLI*
accession n°: P0ACU7
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 973.497 (0), 1040.496 (0), 1307.701 (0), 1534.794 (0)
}
Spot: 2D-001HMA (ecoli4-5)
pI: 5.00 Mw: 20965
%vol: 0.214263 %od: 0.169117
================
*YJDC_ECOLI*
accession n°: P0ACU7
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 973.497 (0), 1040.496 (0), 1307.701 (0), 1534.794 (0)
}
[Click to access protein entry]
Spot: 2D-001HKJ (ecoli4-5)
pI: 4.80 Mw: 32560
%vol: 0.335169 %od: 0.352846
================
*FLGL_ECOLI*
accession n°: P29744
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1129.635 (0), 1138.502 (0), 1144.636 (0), 1156.525 (0),
1264.591 (0), 1323.691 (0), 1564.682 (0), 1580.665 (0), 1601.79 (0),
1685.847 (0), 1701.838 (0), 2147.055 (0), 2274.157 (0), 3241.613 (0)
}
Spot: 2D-001HKJ (ecoli4-5)
pI: 4.80 Mw: 32560
%vol: 0.335169 %od: 0.352846
================
*FLGL_ECOLI*
accession n°: P29744
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1129.635 (0), 1138.502 (0), 1144.636 (0), 1156.525 (0),
1264.591 (0), 1323.691 (0), 1564.682 (0), 1580.665 (0), 1601.79 (0),
1685.847 (0), 1701.838 (0), 2147.055 (0), 2274.157 (0), 3241.613 (0)
}
[Click to access protein entry]
Spot: 2D-001HFT (ecoli4-5)
pI: 4.97 Mw: 61125
%vol: 0.746349 %od: 0.515438
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 875.438 (0), 985.527 (0), 1011.535 (0), 1030.555 (0),
1045.554 (0), 1050.516 (0), 1199.665 (0), 1217.623 (0), 1233.63 (0),
1238.67 (0), 1373.743 (0), 1389.724 (0), 1454.669 (0), 1567.917 (0),
1589.896 (0), 1711.811 (0), 1760.892 (0), 1845.951 (0), 1957.022 (0),
2010.967 (0), 2026.985 (0), 2402.256 (0), 2851.322 (0), 2867.308 (0),
3239.755 (0) }
================
*DNAK_ECOLI*
accession n: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1050.487 (0), 1149.638 (0), 1179.593 (0), 1206.582 (0),
1277.671 (0), 1395.742 (0), 1485.806 (0), 1500.777 (0), 1598.838 (0),
2281.021 (0), 2441.302 (0), 2653.295 (0) }
Spot: 2D-001HFT (ecoli4-5)
pI: 4.97 Mw: 61125
%vol: 0.746349 %od: 0.515438
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 875.438 (0), 985.527 (0), 1011.535 (0), 1030.555 (0),
1045.554 (0), 1050.516 (0), 1199.665 (0), 1217.623 (0), 1233.63 (0),
1238.67 (0), 1373.743 (0), 1389.724 (0), 1454.669 (0), 1567.917 (0),
1589.896 (0), 1711.811 (0), 1760.892 (0), 1845.951 (0), 1957.022 (0),
2010.967 (0), 2026.985 (0), 2402.256 (0), 2851.322 (0), 2867.308 (0),
3239.755 (0) }
================
*DNAK_ECOLI*
accession n: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1050.487 (0), 1149.638 (0), 1179.593 (0), 1206.582 (0),
1277.671 (0), 1395.742 (0), 1485.806 (0), 1500.777 (0), 1598.838 (0),
2281.021 (0), 2441.302 (0), 2653.295 (0) }
[Click to access protein entry]
Spot: 2D-001HJQ (ecoli4-5)
pI: 4.83 Mw: 39220
%vol: 0.416281 %od: 0.346485
================
*FTSZ_ECOLI*
accession n°: P0A9A6
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1097.591 (0), 1100.58 (0), 1116.568 (0), 1245.619 (0),
1374.852 (0), 1393.768 (0), 1424.794 (0), 1440.783 (0), 1448.831 (0),
1603.975 (0), 1608.936 (0), 1624.912 (0), 1880.071 (0), 2008.178 (0),
2048.284 (0), 2165.211 (0), 2342.426 (0), 2404.336 (0), 2542.484 (0),
2551.37 (0), 2586.492 (0) }
================
*GALM_ECOLI*
accession n: P0A9C3
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1064.558 (0), 1086.519 (0), 1172.604 (0), 1262.595 (0),
1492.706 (0), 1772.846 (0), 1788.861 (0), 2347.152 (0), 2684.218 (0)
}
Spot: 2D-001HJQ (ecoli4-5)
pI: 4.83 Mw: 39220
%vol: 0.416281 %od: 0.346485
================
*FTSZ_ECOLI*
accession n°: P0A9A6
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1097.591 (0), 1100.58 (0), 1116.568 (0), 1245.619 (0),
1374.852 (0), 1393.768 (0), 1424.794 (0), 1440.783 (0), 1448.831 (0),
1603.975 (0), 1608.936 (0), 1624.912 (0), 1880.071 (0), 2008.178 (0),
2048.284 (0), 2165.211 (0), 2342.426 (0), 2404.336 (0), 2542.484 (0),
2551.37 (0), 2586.492 (0) }
================
*GALM_ECOLI*
accession n: P0A9C3
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1064.558 (0), 1086.519 (0), 1172.604 (0), 1262.595 (0),
1492.706 (0), 1772.846 (0), 1788.861 (0), 2347.152 (0), 2684.218 (0)
}
[Click to access protein entry]
Spot: 2D-001HMJ (ecoli4-5)
pI: 4.96 Mw: 19503
%vol: 0.118865 %od: 0.019029
================
*NFUA_ECOLI*
accession n°: P63020
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 898.448 (0), 1158.587 (0), 1230.666 (0), 1371.716 (0),
2098.022 (0), 2114.032 (0) }
Spot: 2D-001HMJ (ecoli4-5)
pI: 4.96 Mw: 19503
%vol: 0.118865 %od: 0.019029
================
*NFUA_ECOLI*
accession n°: P63020
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 898.448 (0), 1158.587 (0), 1230.666 (0), 1371.716 (0),
2098.022 (0), 2114.032 (0) }
[Click to access protein entry]
Spot: 2D-001HM3 (ecoli4-5)
pI: 4.93 Mw: 22242
%vol: 0.555043 %od: 0.905686
================
*CYSK_ECOLI*
accession n°: P0ABK5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1210.556 (0), 1283.749 (0), 1473.817 (0), 1618.845 (0),
1626.928 (0), 2117.189 (0), 2141.107 (0), 2257.253 (0), 3235.628 (0)
}
Spot: 2D-001HM3 (ecoli4-5)
pI: 4.93 Mw: 22242
%vol: 0.555043 %od: 0.905686
================
*CYSK_ECOLI*
accession n°: P0ABK5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1210.556 (0), 1283.749 (0), 1473.817 (0), 1618.845 (0),
1626.928 (0), 2117.189 (0), 2141.107 (0), 2257.253 (0), 3235.628 (0)
}
[Click to access protein entry]
Spot: 2D-001HON (ecoli4-5)
pI: 5.01 Mw: 11128
%vol: 0.294357 %od: 0.395884
================
*TPIS_ECOLI*
accession n°: P0A858
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 864.338 (0), 933.475 (0), 999.529 (0), 1208.595 (0),
2245.012 (0), 2407.163 (0), 3090.423 (0) }
================
*GRCA_ECOLI*
accession n: P68066
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 890.475 (0), 1219.58 (0), 1280.686 (0), 1381.727 (0),
1434.77 (0) }
Spot: 2D-001HON (ecoli4-5)
pI: 5.01 Mw: 11128
%vol: 0.294357 %od: 0.395884
================
*TPIS_ECOLI*
accession n°: P0A858
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 864.338 (0), 933.475 (0), 999.529 (0), 1208.595 (0),
2245.012 (0), 2407.163 (0), 3090.423 (0) }
================
*GRCA_ECOLI*
accession n: P68066
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 890.475 (0), 1219.58 (0), 1280.686 (0), 1381.727 (0),
1434.77 (0) }
[Click to access protein entry]
Spot: 2D-001HFK (ecoli4-5)
pI: 4.99 Mw: 64780
%vol: 1.02999 %od: 1.18878
================
*RS1_ECOLI*
accession n°: P0AG67
Identification Methods:
* MAPPING: {Gm}
Spot: 2D-001HFK (ecoli4-5)
pI: 4.99 Mw: 64780
%vol: 1.02999 %od: 1.18878
================
*RS1_ECOLI*
accession n°: P0AG67
Identification Methods:
* MAPPING: {Gm}
[Click to access protein entry]
Spot: 2D-001HPA (ecoli4-5)
pI: 4.99 Mw: 10511
%vol: 0.232628 %od: 0.538865
================
*HISJ_ECOLI*
accession n°: P0AEU0
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 903.396 (0), 1107.575 (0), 1123.554 (0), 1210.491 (0),
1810.911 (0), 2199.188 (0), 2299.245 (0), 2355.312 (0)
}
Spot: 2D-001HPA (ecoli4-5)
pI: 4.99 Mw: 10511
%vol: 0.232628 %od: 0.538865
================
*HISJ_ECOLI*
accession n°: P0AEU0
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 903.396 (0), 1107.575 (0), 1123.554 (0), 1210.491 (0),
1810.911 (0), 2199.188 (0), 2299.245 (0), 2355.312 (0)
}
[Click to access protein entry]
Spot: 2D-001HLU (ecoli4-5)
pI: 4.95 Mw: 24067
%vol: 0.499946 %od: 0.655584
================
*CYSK_ECOLI*
accession n°: P0ABK5
Identification Methods:
* MAPPING: {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1210.568 (0), 1256.713 (0), 1283.76 (0), 1473.841 (0),
1618.859 (0), 1626.927 (0), 2117.18 (0), 2141.142 (0), 2257.298 (0),
3235.678 (0), 3367.89 (0) }
Spot: 2D-001HLU (ecoli4-5)
pI: 4.95 Mw: 24067
%vol: 0.499946 %od: 0.655584
================
*CYSK_ECOLI*
accession n°: P0ABK5
Identification Methods:
* MAPPING: {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1210.568 (0), 1256.713 (0), 1283.76 (0), 1473.841 (0),
1618.859 (0), 1626.927 (0), 2117.18 (0), 2141.142 (0), 2257.298 (0),
3235.678 (0), 3367.89 (0) }
[Click to access protein entry]
Spot: 2D-001HN9 (ecoli4-5)
pI: 4.86 Mw: 14849
%vol: 0.160697 %od: 0.266134
================
*PTGA_ECOLI*
accession n°: P69783
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 891.435 (0), 958.512 (0), 1087.556 (0), 1103.603 (0),
1382.806 (0), 1414.806 (0), 1646.84 (0), 1662.849 (0), 1816.946 (0),
2044.122 (0), 2130.177 (0), 2146.133 (0) }
Spot: 2D-001HN9 (ecoli4-5)
pI: 4.86 Mw: 14849
%vol: 0.160697 %od: 0.266134
================
*PTGA_ECOLI*
accession n°: P69783
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 891.435 (0), 958.512 (0), 1087.556 (0), 1103.603 (0),
1382.806 (0), 1414.806 (0), 1646.84 (0), 1662.849 (0), 1816.946 (0),
2044.122 (0), 2130.177 (0), 2146.133 (0) }
[Click to access protein entry]
Spot: 2D-001HGU (ecoli4-5)
pI: 4.95 Mw: 55185
%vol: 0.996832 %od: 0.868375
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 875.466 (0), 921.509 (0), 985.573 (0), 1011.54 (0),
1030.584 (0), 1045.564 (0), 1199.675 (0), 1201.626 (0), 1217.62 (0),
1238.684 (0), 1373.726 (0), 1389.709 (0), 1454.66 (0), 1567.899 (0),
1589.884 (0), 1711.782 (0), 1760.888 (0), 1845.925 (0), 1956.987 (0),
2010.943 (0), 2026.94 (0), 2402.219 (0), 2851.258 (0), 3239.653 (0)
}
Spot: 2D-001HGU (ecoli4-5)
pI: 4.95 Mw: 55185
%vol: 0.996832 %od: 0.868375
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 875.466 (0), 921.509 (0), 985.573 (0), 1011.54 (0),
1030.584 (0), 1045.564 (0), 1199.675 (0), 1201.626 (0), 1217.62 (0),
1238.684 (0), 1373.726 (0), 1389.709 (0), 1454.66 (0), 1567.899 (0),
1589.884 (0), 1711.782 (0), 1760.888 (0), 1845.925 (0), 1956.987 (0),
2010.943 (0), 2026.94 (0), 2402.219 (0), 2851.258 (0), 3239.653 (0)
}
[Click to access protein entry]
Spot: 2D-001HQ8 (ecoli4-5)
pI: 5.00 Mw: 9979
%vol: 0.148453 %od: 0.051671
================
*KAD_ECOLI*
accession n°: P69441
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 834.348 (0), 891.369 (0), 974.458 (0), 1009.599 (0),
1135.588 (0), 1152.559 (0), 1168.575 (0), 1312.816 (0), 1450.769 (0),
1466.749 (0), 2520.331 (0) }
Spot: 2D-001HQ8 (ecoli4-5)
pI: 5.00 Mw: 9979
%vol: 0.148453 %od: 0.051671
================
*KAD_ECOLI*
accession n°: P69441
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 834.348 (0), 891.369 (0), 974.458 (0), 1009.599 (0),
1135.588 (0), 1152.559 (0), 1168.575 (0), 1312.816 (0), 1450.769 (0),
1466.749 (0), 2520.331 (0) }
[Click to access protein entry]
Spot: 2D-001HMI (ecoli4-5)
pI: 4.72 Mw: 19761
%vol: 0.324966 %od: 0.56411
================
*NFUA_ECOLI*
accession n°: P63020
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 898.431 (0), 1116.552 (0), 1132.533 (0), 1158.591 (0),
1230.673 (0), 1260.67 (0), 1371.744 (0), 2098.079 (0), 2114.049 (0)
}
Spot: 2D-001HMI (ecoli4-5)
pI: 4.72 Mw: 19761
%vol: 0.324966 %od: 0.56411
================
*NFUA_ECOLI*
accession n°: P63020
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 898.431 (0), 1116.552 (0), 1132.533 (0), 1158.591 (0),
1230.673 (0), 1260.67 (0), 1371.744 (0), 2098.079 (0), 2114.049 (0)
}
[Click to access protein entry]
Spot: 2D-001HN3 (ecoli4-5)
pI: 5.02 Mw: 15095
%vol: 1.00601 %od: 2.24541
================
*TPX_ECOLI*
accession n°: P0A862
Identification Methods:
* MAPPING: {Gm}
Spot: 2D-001HN3 (ecoli4-5)
pI: 5.02 Mw: 15095
%vol: 1.00601 %od: 2.24541
================
*TPX_ECOLI*
accession n°: P0A862
Identification Methods:
* MAPPING: {Gm}
[Click to access protein entry]
Spot: 2D-001HQK (ecoli4-5)
pI: 4.71 Mw: 9775
%vol: 1.33353 %od: 6.59359
================
*RL7_ECOLI*
accession n°: P0A7K2
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 964.489 (0), 1113.584 (0), 1244.615 (0), 1476.78 (0),
2015.042 (0), 2737.296 (0), 2769.251 (0) }
Spot: 2D-001HQK (ecoli4-5)
pI: 4.71 Mw: 9775
%vol: 1.33353 %od: 6.59359
================
*RL7_ECOLI*
accession n°: P0A7K2
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 964.489 (0), 1113.584 (0), 1244.615 (0), 1476.78 (0),
2015.042 (0), 2737.296 (0), 2769.251 (0) }
[Click to access protein entry]
Spot: 2D-001HJ1 (ecoli4-5)
pI: 4.55 Mw: 43745
%vol: 0.231098 %od: 0.0368767
================
*ATPB_ECOLI*
accession n°: P0ABB4
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 900.551 (0), 918.458 (0), 1107.594 (0), 1122.619 (0),
1263.73 (0), 1332.747 (0), 1366.782 (0), 1450.851 (0), 1506.781 (0),
1609.017 (0), 1660.888 (0), 1676.887 (0), 1824.043 (0), 1840.995 (0)
}
Spot: 2D-001HJ1 (ecoli4-5)
pI: 4.55 Mw: 43745
%vol: 0.231098 %od: 0.0368767
================
*ATPB_ECOLI*
accession n°: P0ABB4
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 900.551 (0), 918.458 (0), 1107.594 (0), 1122.619 (0),
1263.73 (0), 1332.747 (0), 1366.782 (0), 1450.851 (0), 1506.781 (0),
1609.017 (0), 1660.888 (0), 1676.887 (0), 1824.043 (0), 1840.995 (0)
}
[Click to access protein entry]
Spot: 2D-001HKK (ecoli4-5)
pI: 4.83 Mw: 32453
%vol: 0.174471 %od: 0.0250449
================
*FLGL_ECOLI*
accession n°: P29744
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 861.414 (0), 1129.61 (0), 1138.527 (0), 1144.625 (0),
1525.747 (0), 1580.638 (0), 1601.778 (0), 1612.622 (0), 1701.826 (0),
1851.827 (0), 2147.037 (0), 2274.161 (0), 3241.692 (0)
}
Spot: 2D-001HKK (ecoli4-5)
pI: 4.83 Mw: 32453
%vol: 0.174471 %od: 0.0250449
================
*FLGL_ECOLI*
accession n°: P29744
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 861.414 (0), 1129.61 (0), 1138.527 (0), 1144.625 (0),
1525.747 (0), 1580.638 (0), 1601.778 (0), 1612.622 (0), 1701.826 (0),
1851.827 (0), 2147.037 (0), 2274.161 (0), 3241.692 (0)
}
[Click to access protein entry]
Spot: 2D-001HHU (ecoli4-5)
pI: 4.95 Mw: 47782
%vol: 0.127027 %od: 0.0700821
================
*ATPB_ECOLI*
accession n°: P0ABB4
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1366.714 (0), 1450.812 (0), 1506.716 (0), 1608.946 (0),
1676.778 (0), 1790.852 (0), 1905.953 (0), 2151.245 (0)
}
Spot: 2D-001HHU (ecoli4-5)
pI: 4.95 Mw: 47782
%vol: 0.127027 %od: 0.0700821
================
*ATPB_ECOLI*
accession n°: P0ABB4
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1366.714 (0), 1450.812 (0), 1506.716 (0), 1608.946 (0),
1676.778 (0), 1790.852 (0), 1905.953 (0), 2151.245 (0)
}
[Click to access protein entry]
Spot: 2D-001HFX (ecoli4-5)
pI: 4.96 Mw: 60841
%vol: 0.278031 %od: 0.184238
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {Gm}
Spot: 2D-001HFX (ecoli4-5)
pI: 4.96 Mw: 60841
%vol: 0.278031 %od: 0.184238
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {Gm}
[Click to access protein entry]
Spot: 2D-001HNL (ecoli4-5)
pI: 4.95 Mw: 13907
%vol: 0.746859 %od: 1.56669
================
*GREA_ECOLI*
accession n°: P0A6W5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1045.541 (0), 1110.507 (0), 1309.776 (0), 2370.181 (0)
}
================
*PTGA_ECOLI*
accession n: P69783
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1382.78 (0), 1414.81 (0), 1646.908 (0), 1662.84 (0),
1816.961 (0), 3083.468 (0), 3380.696 (0) }
Spot: 2D-001HNL (ecoli4-5)
pI: 4.95 Mw: 13907
%vol: 0.746859 %od: 1.56669
================
*GREA_ECOLI*
accession n°: P0A6W5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1045.541 (0), 1110.507 (0), 1309.776 (0), 2370.181 (0)
}
================
*PTGA_ECOLI*
accession n: P69783
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1382.78 (0), 1414.81 (0), 1646.908 (0), 1662.84 (0),
1816.961 (0), 3083.468 (0), 3380.696 (0) }
[Click to access protein entry]
Spot: 2D-001HOI (ecoli4-5)
pI: 4.95 Mw: 11539
%vol: 0.472397 %od: 1.16891
================
*METQ_ECOLI*
accession n°: P28635
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1264.724 (0), 1290.703 (0), 1861.885 (0), 1989.982 (0),
2194.196 (0), 2325.203 (0), 2674.464 (0) }
Spot: 2D-001HOI (ecoli4-5)
pI: 4.95 Mw: 11539
%vol: 0.472397 %od: 1.16891
================
*METQ_ECOLI*
accession n°: P28635
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1264.724 (0), 1290.703 (0), 1861.885 (0), 1989.982 (0),
2194.196 (0), 2325.203 (0), 2674.464 (0) }
[Click to access protein entry]
Spot: 2D-001HFV (ecoli4-5)
pI: 4.95 Mw: 60700
%vol: 0.656562 %od: 1.07755
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 960.496 (0), 1050.494 (0), 1061.45 (0), 1149.622 (0),
1179.621 (0), 1206.593 (0), 1277.647 (0), 1286.673 (0), 1395.79 (0),
1485.829 (0), 1500.788 (0), 1598.84 (0), 1659.903 (0), 1816.009 (0),
2423.278 (0), 2441.29 (0), 2653.297 (0) }
Spot: 2D-001HFV (ecoli4-5)
pI: 4.95 Mw: 60700
%vol: 0.656562 %od: 1.07755
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 960.496 (0), 1050.494 (0), 1061.45 (0), 1149.622 (0),
1179.621 (0), 1206.593 (0), 1277.647 (0), 1286.673 (0), 1395.79 (0),
1485.829 (0), 1500.788 (0), 1598.84 (0), 1659.903 (0), 1816.009 (0),
2423.278 (0), 2441.29 (0), 2653.297 (0) }
[Click to access protein entry]
Spot: 2D-001HN8 (ecoli4-5)
pI: 4.95 Mw: 14800
%vol: 1.17896 %od: 4.25687
================
*PTGA_ECOLI*
accession n°: P69783
Identification Methods:
* MAPPING: {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 958.508 (0), 1087.575 (0), 1103.539 (0), 1382.771 (0),
1414.777 (0), 1646.816 (0), 1662.788 (0), 1816.889 (0), 2044.026 (0),
2130.075 (0), 3083.376 (0), 3380.466 (0) }
Spot: 2D-001HN8 (ecoli4-5)
pI: 4.95 Mw: 14800
%vol: 1.17896 %od: 4.25687
================
*PTGA_ECOLI*
accession n°: P69783
Identification Methods:
* MAPPING: {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 958.508 (0), 1087.575 (0), 1103.539 (0), 1382.771 (0),
1414.777 (0), 1646.816 (0), 1662.788 (0), 1816.889 (0), 2044.026 (0),
2130.075 (0), 3083.376 (0), 3380.466 (0) }
[Click to access protein entry]
Spot: 2D-001HMO (ecoli4-5)
pI: 5.01 Mw: 18505
%vol: 0.191306 %od: 0.113448
================
*BCCP_ECOLI*
accession n°: P0ABD8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 891.514 (0), 1057.548 (0), 1073.535 (0), 1079.537 (0),
1095.509 (0), 2546.288 (0), 2674.371 (0) }
Spot: 2D-001HMO (ecoli4-5)
pI: 5.01 Mw: 18505
%vol: 0.191306 %od: 0.113448
================
*BCCP_ECOLI*
accession n°: P0ABD8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 891.514 (0), 1057.548 (0), 1073.535 (0), 1079.537 (0),
1095.509 (0), 2546.288 (0), 2674.371 (0) }
[Click to access protein entry]
Spot: 2D-001HHV (ecoli4-5)
pI: 4.97 Mw: 47893
%vol: 0.131108 %od: 0.066538
================
*TIG_ECOLI*
accession n°: P0A850
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 826.427 (0), 944.461 (0), 1027.496 (0), 1149.52 (0),
1264.62 (0), 1266.781 (0), 1428.675 (0), 1445.782 (0), 1583.863 (0),
2039.031 (0) }
Spot: 2D-001HHV (ecoli4-5)
pI: 4.97 Mw: 47893
%vol: 0.131108 %od: 0.066538
================
*TIG_ECOLI*
accession n°: P0A850
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 826.427 (0), 944.461 (0), 1027.496 (0), 1149.52 (0),
1264.62 (0), 1266.781 (0), 1428.675 (0), 1445.782 (0), 1583.863 (0),
2039.031 (0) }
[Click to access protein entry]
Spot: 2D-001HOT (ecoli4-5)
pI: 4.96 Mw: 10675
%vol: 0.212222 %od: 0.169735
================
*GRCA_ECOLI*
accession n°: P68066
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 865.46 (0), 890.571 (0), 1219.673 (0), 1280.782 (0),
1381.807 (0), 1434.842 (0) }
Spot: 2D-001HOT (ecoli4-5)
pI: 4.96 Mw: 10675
%vol: 0.212222 %od: 0.169735
================
*GRCA_ECOLI*
accession n°: P68066
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 865.46 (0), 890.571 (0), 1219.673 (0), 1280.782 (0),
1381.807 (0), 1434.842 (0) }
[Click to access protein entry]
Spot: 2D-001HK8 (ecoli4-5)
pI: 4.98 Mw: 35245
%vol: 0.167839 %od: 0.157903
================
*HLDD_ECOLI*
accession n°: P67910
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1015.492 (0), 1088.542 (0), 1540.766 (0), 1571.868 (0),
1702.831 (0), 1721.899 (0) }
Spot: 2D-001HK8 (ecoli4-5)
pI: 4.98 Mw: 35245
%vol: 0.167839 %od: 0.157903
================
*HLDD_ECOLI*
accession n°: P67910
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1015.492 (0), 1088.542 (0), 1540.766 (0), 1571.868 (0),
1702.831 (0), 1721.899 (0) }
[Click to access protein entry]
Spot: 2D-001HMN (ecoli4-5)
pI: 4.74 Mw: 18383
%vol: 0.47954 %od: 1.18727
================
*BCCP_ECOLI*
accession n°: P0ABD8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 891.452 (0), 1057.505 (0), 1073.482 (0), 1079.478 (0),
2546.25 (0), 2674.313 (0) }
Spot: 2D-001HMN (ecoli4-5)
pI: 4.74 Mw: 18383
%vol: 0.47954 %od: 1.18727
================
*BCCP_ECOLI*
accession n°: P0ABD8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 891.452 (0), 1057.505 (0), 1073.482 (0), 1079.478 (0),
2546.25 (0), 2674.313 (0) }
[Click to access protein entry]
Spot: 2D-001HLC (ecoli4-5)
pI: 5.01 Mw: 26299
%vol: 0.152025 %od: 0.145744
================
*CYSK_ECOLI*
accession n°: P0ABK5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1210.533 (0), 1283.729 (0), 1473.808 (0), 1618.813 (0),
1626.891 (0), 2141.093 (0), 3235.617 (0), 3367.823 (0)
}
Spot: 2D-001HLC (ecoli4-5)
pI: 5.01 Mw: 26299
%vol: 0.152025 %od: 0.145744
================
*CYSK_ECOLI*
accession n°: P0ABK5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1210.533 (0), 1283.729 (0), 1473.808 (0), 1618.813 (0),
1626.891 (0), 2141.093 (0), 3235.617 (0), 3367.823 (0)
}
[Click to access protein entry]
Spot: 2D-001HQI (ecoli4-5)
pI: 4.84 Mw: 9800
%vol: 1.17283 %od: 1.73115
================
*MOG_ECOLI*
accession n°: P0AF03
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 959.569 (0), 1181.564 (0), 1197.528 (0), 1343.712 (0),
1581.996 (0), 2474.409 (0) }
Spot: 2D-001HQI (ecoli4-5)
pI: 4.84 Mw: 9800
%vol: 1.17283 %od: 1.73115
================
*MOG_ECOLI*
accession n°: P0AF03
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 959.569 (0), 1181.564 (0), 1197.528 (0), 1343.712 (0),
1581.996 (0), 2474.409 (0) }
[Click to access protein entry]
Spot: 2D-001HFS (ecoli4-5)
pI: 4.96 Mw: 61267
%vol: 0.226506 %od: 0.189
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1003.523 (0), 1021.412 (0), 1149.593 (0), 1179.583 (0),
1201.628 (0), 1206.499 (0), 1277.664 (0), 1286.622 (0), 1485.845 (0),
1598.815 (0), 2281.059 (0) }
Spot: 2D-001HFS (ecoli4-5)
pI: 4.96 Mw: 61267
%vol: 0.226506 %od: 0.189
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1003.523 (0), 1021.412 (0), 1149.593 (0), 1179.583 (0),
1201.628 (0), 1206.499 (0), 1277.664 (0), 1286.622 (0), 1485.845 (0),
1598.815 (0), 2281.059 (0) }
[Click to access protein entry]
Spot: 2D-001HOB (ecoli4-5)
pI: 4.95 Mw: 11934
%vol: 0.187225 %od: 0.3778
================
*METQ_ECOLI*
accession n°: P28635
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1264.738 (0), 1290.716 (0), 1861.846 (0), 1989.911 (0),
2194.134 (0), 2325.126 (0), 2674.368 (0) }
Spot: 2D-001HOB (ecoli4-5)
pI: 4.95 Mw: 11934
%vol: 0.187225 %od: 0.3778
================
*METQ_ECOLI*
accession n°: P28635
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1264.738 (0), 1290.716 (0), 1861.846 (0), 1989.911 (0),
2194.134 (0), 2325.126 (0), 2674.368 (0) }
[Click to access protein entry]
Spot: 2D-001HF6 (ecoli4-5)
pI: 4.98 Mw: 70671
%vol: 0.589223 %od: 0.228948
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 960.426 (0), 1050.465 (0), 1061.464 (0), 1149.622 (0),
1179.618 (0), 1206.577 (0), 1277.649 (0), 1290.625 (0), 1395.785 (0),
1485.839 (0), 1598.843 (0), 1659.873 (0), 1816.005 (0), 2346.269 (0),
2423.302 (0), 2441.293 (0), 2532.246 (0), 2653.302 (0), 2869.353 (0)
}
Spot: 2D-001HF6 (ecoli4-5)
pI: 4.98 Mw: 70671
%vol: 0.589223 %od: 0.228948
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 960.426 (0), 1050.465 (0), 1061.464 (0), 1149.622 (0),
1179.618 (0), 1206.577 (0), 1277.649 (0), 1290.625 (0), 1395.785 (0),
1485.839 (0), 1598.843 (0), 1659.873 (0), 1816.005 (0), 2346.269 (0),
2423.302 (0), 2441.293 (0), 2532.246 (0), 2653.302 (0), 2869.353 (0)
}
[Click to access protein entry]
Spot: 2D-001HLH (ecoli4-5)
pI: 4.95 Mw: 25617
%vol: 0.13621 %od: 0.157612
================
*CYSK_ECOLI*
accession n°: P0ABK5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1037.485 (0), 1186.555 (0), 1210.541 (0), 1256.682 (0),
1283.73 (0), 1473.805 (0), 1618.816 (0), 1626.913 (0), 2141.118 (0),
2257.262 (0), 3235.652 (0) }
Spot: 2D-001HLH (ecoli4-5)
pI: 4.95 Mw: 25617
%vol: 0.13621 %od: 0.157612
================
*CYSK_ECOLI*
accession n°: P0ABK5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1037.485 (0), 1186.555 (0), 1210.541 (0), 1256.682 (0),
1283.73 (0), 1473.805 (0), 1618.816 (0), 1626.913 (0), 2141.118 (0),
2257.262 (0), 3235.652 (0) }
[Click to access protein entry]
Spot: 2D-001HIB (ecoli4-5)
pI: 4.61 Mw: 45507
%vol: 0.329556 %od: 0.241798
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 931.474 (0), 1036.555 (0), 1101.54 (0), 1191.621 (0),
1420.768 (0), 1440.821 (0), 1561.832 (0), 1614.842 (0), 1742.943 (0),
2085.097 (0), 2249.106 (0), 2338.153 (0), 2566.246 (0), 2629.268 (0)
}
Spot: 2D-001HIB (ecoli4-5)
pI: 4.61 Mw: 45507
%vol: 0.329556 %od: 0.241798
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 931.474 (0), 1036.555 (0), 1101.54 (0), 1191.621 (0),
1420.768 (0), 1440.821 (0), 1561.832 (0), 1614.842 (0), 1742.943 (0),
2085.097 (0), 2249.106 (0), 2338.153 (0), 2566.246 (0), 2629.268 (0)
}
[Click to access protein entry]
Spot: 2D-001HR2 (ecoli4-5)
pI: 4.84 Mw: 9475
%vol: 1.16467 %od: 2.53955
================
*HDEA_ECOLI*
accession n°: P0AES9
Identification Methods:
* MAPPING: {Mi,PMF}
peptide masses: { (TRYPSIN)
$m/Z= 861.461 (0), 2982.249 (0), 3584.995 (0) }
Spot: 2D-001HR2 (ecoli4-5)
pI: 4.84 Mw: 9475
%vol: 1.16467 %od: 2.53955
================
*HDEA_ECOLI*
accession n°: P0AES9
Identification Methods:
* MAPPING: {Mi,PMF}
peptide masses: { (TRYPSIN)
$m/Z= 861.461 (0), 2982.249 (0), 3584.995 (0) }
[Click to access protein entry]
Spot: 2D-001HHI (ecoli4-5)
pI: 4.96 Mw: 49707
%vol: 0.360164 %od: 0.251667
================
*TIG_ECOLI*
accession n°: P0A850
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 944.461 (0), 1027.524 (0), 1149.595 (0), 1264.677 (0),
1266.732 (0) }
Spot: 2D-001HHI (ecoli4-5)
pI: 4.96 Mw: 49707
%vol: 0.360164 %od: 0.251667
================
*TIG_ECOLI*
accession n°: P0A850
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 944.461 (0), 1027.524 (0), 1149.595 (0), 1264.677 (0),
1266.732 (0) }
[Click to access protein entry]
Spot: 2D-001HQO (ecoli4-5)
pI: 4.95 Mw: 9749
%vol: 0.630035 %od: 0.823031
================
*CHEY_ECOLI*
accession n°: P0AE67
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1329.686 (0), 1345.666 (0), 1501.756 (0), 1806.888 (0),
2062.984 (0), 2749.411 (0) }
Spot: 2D-001HQO (ecoli4-5)
pI: 4.95 Mw: 9749
%vol: 0.630035 %od: 0.823031
================
*CHEY_ECOLI*
accession n°: P0AE67
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1329.686 (0), 1345.666 (0), 1501.756 (0), 1806.888 (0),
2062.984 (0), 2749.411 (0) }
[Click to access protein entry]
Spot: 2D-001HGK (ecoli4-5)
pI: 4.99 Mw: 56877
%vol: 1.16059 %od: 1.67706
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 875.403 (0), 1011.518 (0), 1045.563 (0), 1238.657 (0),
1373.698 (0), 1454.662 (0), 1567.901 (0), 1711.785 (0), 1769.916 (0),
1798.985 (0), 1845.934 (0), 2010.945 (0), 2026.953 (0), 2399.304 (0),
2402.255 (0), 2851.301 (0) }
Spot: 2D-001HGK (ecoli4-5)
pI: 4.99 Mw: 56877
%vol: 1.16059 %od: 1.67706
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 875.403 (0), 1011.518 (0), 1045.563 (0), 1238.657 (0),
1373.698 (0), 1454.662 (0), 1567.901 (0), 1711.785 (0), 1769.916 (0),
1798.985 (0), 1845.934 (0), 2010.945 (0), 2026.953 (0), 2399.304 (0),
2402.255 (0), 2851.301 (0) }
[Click to access protein entry]
Spot: 2D-001HLF (ecoli4-5)
pI: 4.92 Mw: 25786
%vol: 0.327517 %od: 0.45039
================
*ELBB_ECOLI*
accession n°: P0ABU5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 885.51 (0), 907.509 (0), 1769.822 (0), 2041.999 (0),
2650.406 (0) }
Spot: 2D-001HLF (ecoli4-5)
pI: 4.92 Mw: 25786
%vol: 0.327517 %od: 0.45039
================
*ELBB_ECOLI*
accession n°: P0ABU5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 885.51 (0), 907.509 (0), 1769.822 (0), 2041.999 (0),
2650.406 (0) }
[Click to access protein entry]
Spot: 2D-001HMG (ecoli4-5)
pI: 5.01 Mw: 20288
%vol: 0.232118 %od: 0.05198
================
*SSPB_ECOLI*
accession n°: P0AFZ3
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1060.531 (0), 1195.675 (0), 1399.703 (0), 1570.939 (0)
}
Spot: 2D-001HMG (ecoli4-5)
pI: 5.01 Mw: 20288
%vol: 0.232118 %od: 0.05198
================
*SSPB_ECOLI*
accession n°: P0AFZ3
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1060.531 (0), 1195.675 (0), 1399.703 (0), 1570.939 (0)
}
[Click to access protein entry]
Spot: 2D-001HIJ (ecoli4-5)
pI: 5.00 Mw: 44877
%vol: 0.420363 %od: 0.379327
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1060.621 (0), 1658.841 (0), 1687.835 (0), 2249.112 (0),
2566.222 (0), 2629.291 (0) }
================
*DNAK_ECOLI*
accession n: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1050.475 (0), 1179.617 (0), 1277.693 (0), 1485.839 (0),
2441.327 (0), 2653.326 (0), 2869.412 (0) }
Spot: 2D-001HIJ (ecoli4-5)
pI: 5.00 Mw: 44877
%vol: 0.420363 %od: 0.379327
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1060.621 (0), 1658.841 (0), 1687.835 (0), 2249.112 (0),
2566.222 (0), 2629.291 (0) }
================
*DNAK_ECOLI*
accession n: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1050.475 (0), 1179.617 (0), 1277.693 (0), 1485.839 (0),
2441.327 (0), 2653.326 (0), 2869.412 (0) }
[Click to access protein entry]
Spot: 2D-001HIC (ecoli4-5)
pI: 4.54 Mw: 45507
%vol: 0.302519 %od: 0.210664
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 931.525 (0), 1101.562 (0), 1191.648 (0), 1234.708 (0),
1420.788 (0), 1440.836 (0), 1561.792 (0), 1742.889 (0), 2249.139 (0),
2399.086 (0), 2566.274 (0), 2629.251 (0) }
Spot: 2D-001HIC (ecoli4-5)
pI: 4.54 Mw: 45507
%vol: 0.302519 %od: 0.210664
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 931.525 (0), 1101.562 (0), 1191.648 (0), 1234.708 (0),
1420.788 (0), 1440.836 (0), 1561.792 (0), 1742.889 (0), 2249.139 (0),
2399.086 (0), 2566.274 (0), 2629.251 (0) }
[Click to access protein entry]
Spot: 2D-001HHJ (ecoli4-5)
pI: 4.58 Mw: 49476
%vol: 0.327005 %od: 0.258555
================
*TIG_ECOLI*
accession n°: P0A850
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 826.422 (0), 993.464 (0), 1027.546 (0), 1106.537 (0),
1251.636 (0), 1264.63 (0), 1266.807 (0), 1289.708 (0), 1458.791 (0),
1576.823 (0), 1583.827 (0), 1886.85 (0), 2039.073 (0), 2439.171 (0)
}
Spot: 2D-001HHJ (ecoli4-5)
pI: 4.58 Mw: 49476
%vol: 0.327005 %od: 0.258555
================
*TIG_ECOLI*
accession n°: P0A850
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 826.422 (0), 993.464 (0), 1027.546 (0), 1106.537 (0),
1251.636 (0), 1264.63 (0), 1266.807 (0), 1289.708 (0), 1458.791 (0),
1576.823 (0), 1583.827 (0), 1886.85 (0), 2039.073 (0), 2439.171 (0)
}
[Click to access protein entry]
Spot: 2D-001HFC (ecoli4-5)
pI: 4.98 Mw: 67488
%vol: 1.11927 %od: 1.85278
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 960.411 (0), 1050.447 (0), 1149.595 (0), 1179.6 (0),
1206.555 (0), 1267.677 (0), 1277.607 (0), 1286.662 (0), 1290.585 (0),
1395.761 (0), 1485.812 (0), 1500.727 (0), 1598.828 (0), 1659.867 (0),
1815.982 (0), 2346.221 (0), 2423.265 (0), 2441.28 (0), 2532.252 (0),
2653.281 (0) }
Spot: 2D-001HFC (ecoli4-5)
pI: 4.98 Mw: 67488
%vol: 1.11927 %od: 1.85278
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 960.411 (0), 1050.447 (0), 1149.595 (0), 1179.6 (0),
1206.555 (0), 1267.677 (0), 1277.607 (0), 1286.662 (0), 1290.585 (0),
1395.761 (0), 1485.812 (0), 1500.727 (0), 1598.828 (0), 1659.867 (0),
1815.982 (0), 2346.221 (0), 2423.265 (0), 2441.28 (0), 2532.252 (0),
2653.281 (0) }
[Click to access protein entry]
Spot: 2D-001HKA (ecoli4-5)
pI: 4.76 Mw: 34885
%vol: 0.108662 %od: 0.0205921
================
*POTD_ECOLI*
accession n°: P0AFK9
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 993.512 (0), 1009.51 (0), 1060.564 (0), 1179.603 (0),
1398.835 (0), 1700.874 (0), 1804.87 (0), 1814.784 (0)
}
Spot: 2D-001HKA (ecoli4-5)
pI: 4.76 Mw: 34885
%vol: 0.108662 %od: 0.0205921
================
*POTD_ECOLI*
accession n°: P0AFK9
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 993.512 (0), 1009.51 (0), 1060.564 (0), 1179.603 (0),
1398.835 (0), 1700.874 (0), 1804.87 (0), 1814.784 (0)
}
[Click to access protein entry]
Spot: 2D-001HJR (ecoli4-5)
pI: 4.77 Mw: 39129
%vol: 0.112743 %od: 0.062067
================
*FTSZ_ECOLI*
accession n°: P0A9A6
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1097.559 (0), 1374.771 (0), 1393.691 (0), 1448.715 (0),
1603.827 (0), 1624.805 (0), 1879.933 (0), 2070.016 (0), 2165.087 (0),
2551.126 (0) }
Spot: 2D-001HJR (ecoli4-5)
pI: 4.77 Mw: 39129
%vol: 0.112743 %od: 0.062067
================
*FTSZ_ECOLI*
accession n°: P0A9A6
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1097.559 (0), 1374.771 (0), 1393.691 (0), 1448.715 (0),
1603.827 (0), 1624.805 (0), 1879.933 (0), 2070.016 (0), 2165.087 (0),
2551.126 (0) }
[Click to access protein entry]
Spot: 2D-001HJ0 (ecoli4-5)
pI: 4.95 Mw: 43643
%vol: 0.319353 %od: 0.287217
================
*ATPB_ECOLI*
accession n°: P0ABB4
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 900.518 (0), 1366.767 (0), 1450.804 (0), 1506.752 (0),
1608.969 (0), 1676.814 (0), 1840.897 (0), 1905.971 (0), 2003.052 (0),
2151.196 (0), 2179.13 (0), 2338.165 (0) }
Spot: 2D-001HJ0 (ecoli4-5)
pI: 4.95 Mw: 43643
%vol: 0.319353 %od: 0.287217
================
*ATPB_ECOLI*
accession n°: P0ABB4
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 900.518 (0), 1366.767 (0), 1450.804 (0), 1506.752 (0),
1608.969 (0), 1676.814 (0), 1840.897 (0), 1905.971 (0), 2003.052 (0),
2151.196 (0), 2179.13 (0), 2338.165 (0) }
[Click to access protein entry]
Spot: 2D-001HI8 (ecoli4-5)
pI: 4.58 Mw: 45401
%vol: 0.943776 %od: 3.35994
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 931.655 (0), 1101.685 (0), 1191.739 (0), 1420.87 (0),
1440.9 (0), 1561.925 (0), 1671.795 (0), 1743.002 (0), 1756.967 (0),
2249.12 (0), 2338.13 (0), 2566.202 (0), 2629.238 (0), 3257.566 (0)
}
Spot: 2D-001HI8 (ecoli4-5)
pI: 4.58 Mw: 45401
%vol: 0.943776 %od: 3.35994
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {Mi} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 931.655 (0), 1101.685 (0), 1191.739 (0), 1420.87 (0),
1440.9 (0), 1561.925 (0), 1671.795 (0), 1743.002 (0), 1756.967 (0),
2249.12 (0), 2338.13 (0), 2566.202 (0), 2629.238 (0), 3257.566 (0)
}
[Click to access protein entry]
Spot: 2D-001HH6 (ecoli4-5)
pI: 4.93 Mw: 52435
%vol: 0.327005 %od: 0.177259
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1149.609 (0), 1179.6 (0), 1395.809 (0), 1485.872 (0),
1598.895 (0), 1816.08 (0), 2441.441 (0), 2653.489 (0)
}
Spot: 2D-001HH6 (ecoli4-5)
pI: 4.93 Mw: 52435
%vol: 0.327005 %od: 0.177259
================
*DNAK_ECOLI*
accession n°: P0A6Y8
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1149.609 (0), 1179.6 (0), 1395.809 (0), 1485.872 (0),
1598.895 (0), 1816.08 (0), 2441.441 (0), 2653.489 (0)
}
[Click to access protein entry]
Spot: 2D-001HLY (ecoli4-5)
pI: 4.74 Mw: 22910
%vol: 0.140291 %od: 0.0225186
================
*ENO_ECOLI*
accession n°: P0A6P9
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 950.682 (0), 1189.748 (0), 1562.908 (0), 1605.966 (0),
1928.974 (0), 2118.107 (0), 2776.085 (0) }
Spot: 2D-001HLY (ecoli4-5)
pI: 4.74 Mw: 22910
%vol: 0.140291 %od: 0.0225186
================
*ENO_ECOLI*
accession n°: P0A6P9
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 950.682 (0), 1189.748 (0), 1562.908 (0), 1605.966 (0),
1928.974 (0), 2118.107 (0), 2776.085 (0) }
[Click to access protein entry]
Spot: 2D-001HGR (ecoli4-5)
pI: 4.93 Mw: 55185
%vol: 0.151004 %od: 0.0679375
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1045.564 (0), 1567.964 (0), 1711.869 (0), 1769.995 (0),
1799.061 (0), 1846.024 (0) }
Spot: 2D-001HGR (ecoli4-5)
pI: 4.93 Mw: 55185
%vol: 0.151004 %od: 0.0679375
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1045.564 (0), 1567.964 (0), 1711.869 (0), 1769.995 (0),
1799.061 (0), 1846.024 (0) }
[Click to access protein entry]
Spot: 2D-001HQL (ecoli4-5)
pI: 4.74 Mw: 9851
%vol: 0.242321 %od: 0.0543246
================
*RL7_ECOLI*
accession n°: P0A7K2
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 964.343 (0), 1113.442 (0), 1244.496 (0), 2015.024 (0),
2769.4 (0) }
Spot: 2D-001HQL (ecoli4-5)
pI: 4.74 Mw: 9851
%vol: 0.242321 %od: 0.0543246
================
*RL7_ECOLI*
accession n°: P0A7K2
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 964.343 (0), 1113.442 (0), 1244.496 (0), 2015.024 (0),
2769.4 (0) }
[Click to access protein entry]
Spot: 2D-001HN0 (ecoli4-5)
pI: 4.78 Mw: 15857
%vol: 0.515251 %od: 0.776481
================
*BCCP_ECOLI*
accession n°: P0ABD8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1057.474 (0), 1073.455 (0), 2546.335 (0), 2674.406 (0)
}
Spot: 2D-001HN0 (ecoli4-5)
pI: 4.78 Mw: 15857
%vol: 0.515251 %od: 0.776481
================
*BCCP_ECOLI*
accession n°: P0ABD8
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1057.474 (0), 1073.455 (0), 2546.335 (0), 2674.406 (0)
}
[Click to access protein entry]
Spot: 2D-001HGT (ecoli4-5)
pI: 4.95 Mw: 55185
%vol: 0.342821 %od: 0.25094
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1567.875 (0), 1711.773 (0), 1760.854 (0), 1769.935 (0),
1845.925 (0), 2399.269 (0), 2402.224 (0) }
Spot: 2D-001HGT (ecoli4-5)
pI: 4.95 Mw: 55185
%vol: 0.342821 %od: 0.25094
================
*CH60_ECOLI*
accession n°: P0A6F5
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1567.875 (0), 1711.773 (0), 1760.854 (0), 1769.935 (0),
1845.925 (0), 2399.269 (0), 2402.224 (0) }
[Click to access protein entry]
Spot: 2D-001HIE (ecoli4-5)
pI: 4.87 Mw: 45401
%vol: 0.164778 %od: 0.159793
================
*TIG_ECOLI*
accession n°: P0A850
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 924.386 (0), 933.531 (0), 940.388 (0), 944.504 (0), 993.488 (0),
1014.476 (0), 1106.546 (0), 1122.54 (0), 1133.566 (0), 1149.583 (0),
1204.586 (0), 1251.638 (0), 1264.629 (0), 1266.79 (0), 1289.703 (0),
1420.717 (0), 1422.899 (0), 1445.814 (0), 1576.781 (0), 1583.834 (0),
1719.859 (0), 1833.909 (0), 2039.038 (0), 2195.134 (0), 2439.09 (0),
2829.172 (0) }
Spot: 2D-001HIE (ecoli4-5)
pI: 4.87 Mw: 45401
%vol: 0.164778 %od: 0.159793
================
*TIG_ECOLI*
accession n°: P0A850
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 924.386 (0), 933.531 (0), 940.388 (0), 944.504 (0), 993.488 (0),
1014.476 (0), 1106.546 (0), 1122.54 (0), 1133.566 (0), 1149.583 (0),
1204.586 (0), 1251.638 (0), 1264.629 (0), 1266.79 (0), 1289.703 (0),
1420.717 (0), 1422.899 (0), 1445.814 (0), 1576.781 (0), 1583.834 (0),
1719.859 (0), 1833.909 (0), 2039.038 (0), 2195.134 (0), 2439.09 (0),
2829.172 (0) }
[Click to access protein entry]
Spot: 2D-001HM1 (ecoli4-5)
pI: 4.70 Mw: 22389
%vol: 0.124987 %od: 0.115992
================
*IDH_ECOLI*
accession n°: P08200
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1008.518 (0), 1030.514 (0), 1206.644 (0), 1470.789 (0),
1630.906 (0), 1646.858 (0), 1788.869 (0), 2086.112 (0)
}
Spot: 2D-001HM1 (ecoli4-5)
pI: 4.70 Mw: 22389
%vol: 0.124987 %od: 0.115992
================
*IDH_ECOLI*
accession n°: P08200
Identification Methods:
* MAPPING: {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 1008.518 (0), 1030.514 (0), 1206.644 (0), 1470.789 (0),
1630.906 (0), 1646.858 (0), 1788.869 (0), 2086.112 (0)
}
[Click to access protein entry]
Spot: 2D-001HK9 (ecoli4-5)
pI: 4.95 Mw: 35000
%vol: 0.633606 %od: 0.712271
================
*POTD_ECOLI*
accession n°: P0AFK9
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 993.558 (0), 1009.53 (0), 1060.587 (0), 1085.568 (0),
1150.611 (0), 1179.62 (0), 1307.712 (0), 1310.725 (0), 1398.894 (0),
1700.922 (0), 1709.878 (0), 1798.834 (0), 1804.888 (0), 1814.835 (0),
1819.917 (0), 2197.09 (0), 2451.05 (0) }
Spot: 2D-001HK9 (ecoli4-5)
pI: 4.95 Mw: 35000
%vol: 0.633606 %od: 0.712271
================
*POTD_ECOLI*
accession n°: P0AFK9
Identification Methods:
* MAPPING: {Gm} {PMF}
peptide masses: { (TRYPSIN)
$m/Z= 993.558 (0), 1009.53 (0), 1060.587 (0), 1085.568 (0),
1150.611 (0), 1179.62 (0), 1307.712 (0), 1310.725 (0), 1398.894 (0),
1700.922 (0), 1709.878 (0), 1798.834 (0), 1804.888 (0), 1814.835 (0),
1819.917 (0), 2197.09 (0), 2451.05 (0) }
[Click to access protein entry]
Spot: 2D-001HID (ecoli4-5)
pI: 4.55 Mw: 45507
%vol: 0.431585 %od: 0.355754
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {Mi}
Spot: 2D-001HID (ecoli4-5)
pI: 4.55 Mw: 45507
%vol: 0.431585 %od: 0.355754
================
*FLIC_ECOLI*
accession n°: P04949
Identification Methods:
* MAPPING: {Mi}
SWISS-2DPAGE Viewer
|
Back to the |
-Get more information by dragging your mouse pointer over any highlighted spot -Click on a highlighted spot to access all its associated protein entries
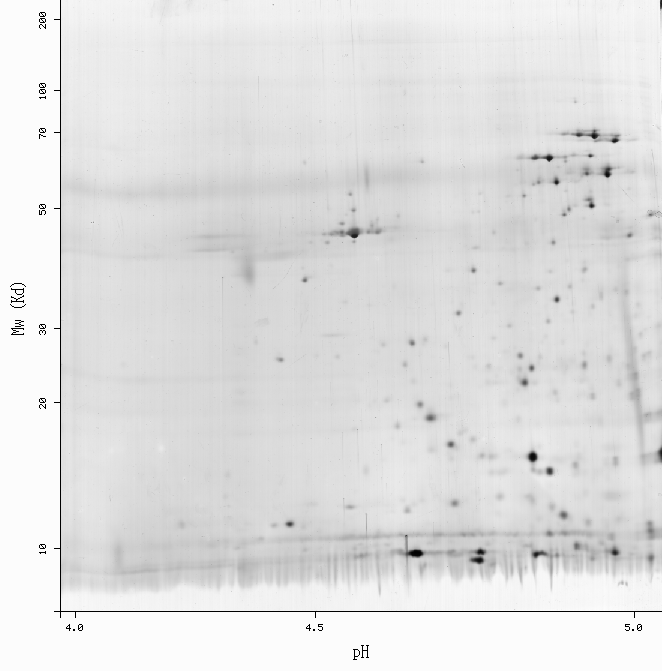
Back to the